Resumen
La contaminación plástica es un importante desafío ambiental de la era contemporánea. El poliestireno (PS), uno de los polímeros plásticos más utilizados en todo el mundo, es muy duradero y difícil de degradar. A pesar de las diversas estrategias de eliminación, el PS sigue afectando a la biodiversidad, la salud humana y los ecosistemas. Recientemente, la comunidad científica se ha centrado en el papel potencial de los microorganismos en la biodegradación del plástico, en particular los del intestino de los insectos plastivoros. En un estudio previo, se aislaron tres cepas bacterianas, cada una representando un grupo taxonómico distinto (Klebsiella, Pseudomonas y Stenotrophomonas), de larvas de Alphitobius diaperinus después de criarlas con una dieta de PS y se enriquecieron en un medio con PS como única fuente de carbono. La cepa de Stenotrophomonas sp., identificada aquí como S. indicatrix, mostró el mayor potencial para la degradación de PS. El presente estudio investiga el perfil genético de la cepa DAI2m/c de S. indicatrix recién aislada a través de la secuenciación del genoma, para identificar genes codificantes de enzimas involucrados en las vías metabólicas intracelulares responsables de la biodegradación del monómero de estireno. Nuestros hallazgos indican que el genoma de la cepa DAI2m/c de S. indicatrix codifica todas las enzimas necesarias para una de las dos vías de degradación del estireno reconocidas, lo que sugiere su capacidad para convertir el estireno en subproductos que luego se utilizan para la producción de energía celular.
Discusión
En ambientes naturales, la biodegradación del PS es notablemente ineficiente debido a multitud de factores bióticos y abióticos, así como a las propiedades intrínsecas del polímero y los aditivos incorporados al plástico; por lo tanto, a menudo tarda décadas o incluso siglos en completarse. La naturaleza persistente de la PS da lugar a una contaminación significativa, problemas de salud y perturbaciones ecológicas. Se ha demostrado que los microorganismos desempeñan un papel crucial en la biodegradación de la PS, y la capacidad de sus enzimas para degradar alcanos de hidrocarburos de petróleo de varias longitudes de cadena ha sido ampliamente documentada en la literatura. Dadas las similitudes estructurales entre los hidrocarburos de petróleo y el polímero PS, las enzimas bacterianas que se sabe que están involucradas en las vías metabólicas de los alcanos, como el alcano 1-monooxigenasa, el citocromo P450 o la alcano hidroxilasa, también pueden participar en la despolimerización extracelular del PS12.
Estudios recientes se han centrado en los mecanismos extracelulares responsables de la degradación de los polímeros PS en oligonucleómeros y monómeros pero no tuvo en cuenta los procesos de degradación secundarios que ocurren una vez que estas moléculas son absorbidas por la célula. Con el fin de llenar este vacío, el presente estudio profundiza en los mecanismos intracelulares que ocurren dentro de la cepa S. indicatrix DAI2m/c recientemente aislada para arrojar luz sobre cómo se incorporan los monómeros de estireno a las vías metabólicas.
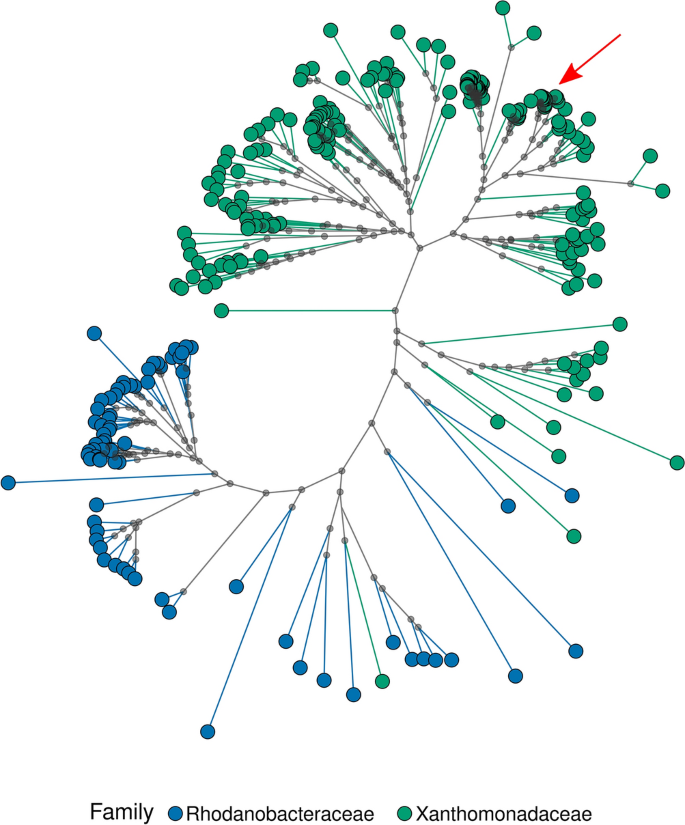
El género Stenotrophomonas es un miembro de la familia Xanthomonadaceae dentro del orden Xanthomonadales, un grupo divergente temprano de Gammaproteobacteria. Los xanthomonadales se dividen en dos familias: Xanthomonadaceae (o Lysobacteriaceae) y Rhodanobacteraceae20. El análisis filogenético utilizando scOGs de BUSCO apoyó una condición parafilética para Rhodanobacteriaceae, mientras que Xanthomonadaceae se identificó como monofilética, excluyendo las posiciones enigmáticas de dos taxones poco estudiados: P. antarcticus y P. arenosa. La primera especie, que formalmente pertenece a la familia Xanthomonadaceae, fue propuesta recientemente por algunos autores para ser reasignados a las Rhodanobacteriaceae. Hasta donde sabemos, no se dispone de datos sistemáticos y/o filogenéticos, a su vez, para P. arenosa. El análisis filogenético también permitió esclarecer la posición sistemática de la recién identificada S. indicatrix DAI2m/c como parte del género Stenotrophomonas (Fig. 4, Fig. Suplementaria. 4).
Como se describe en la base de datos de vías KEGG (entrada: map00643) y en el mapa de vías de estireno BBD, los monómeros de estireno, después de la absorción, ingresan a dos vías metabólicas primarias, identificadas en este estudio como ruta A y ruta B (Fig. 3). En la vía A, la estireno monooxigenasa [EC:1.14.14.11] es la primera enzima que interactúa con el monómero de estireno. La actividad de una cascada de siete enzimas adicionales da como resultado la formación de dos subproductos finales del metabolismo del estireno, fumarato y acetoacetato, que ingresan como sustratos en el ciclo del ácido cítrico y el metabolismo del propanoato, respectivamente. En la vía B, una oxidorreductasa [EC 1.14.12.-] convierte el monómero de estireno en estireno-cis-2,3-dihidrodiol. Este intermediario es procesado posteriormente por tres enzimas para producir acrilato y 2-hidroxipenta-2,4-dienoato. En la subvía B1, el acrilato se convierte en L-lactato por la acción de tres enzimas, que luego ingresa al metabolismo del piruvato. En la subvía B2, el 2-hidroxipenta-2,4-dienoato se convierte por la actividad de dos enzimas en acetaldehído y piruvato como subproductos finales. Estos últimos están directamente implicados en múltiples vías metabólicas posteriores.
La anotación funcional automática reveló la presencia de cinco genes que codifican enzimas en la vía de biodegradación del estireno, cuatro de los cuales pertenecen a la vía A y uno a la vía B (Fig. 3, Fig. Suplementaria. 2a). La curación manual posterior de las anotaciones utilizando perfiles de Pfam confirmó la atribución de esas enzimas y condujo a la identificación de seis enzimas suplementarias pertenecientes a la vía B (Fig. 3, Fig. 2b). Por último, la 4-hidroxi-2-oxovalerato aldolasa [EC:4.1.3.39] y dos oxidorreductasas [EC:1.14.12.-; 1.14.13.-] se identificaron parcialmente debido a su falta de especificidad en el dominio proteico. De hecho, solo se recuperó una proporción de dominios característicos de Pfam en el genoma de S. indicatrix DAI2m/c (66,7%, 50,0% y 52,5%, respectivamente).
Los genes que codifican para todas las enzimas en la vía B de biodegradación del estireno se identificaron en el cromosoma de S. indicatrix DAI2m/c, mientras que solo cinco de los ocho se identificaron en la vía A (Fig. 3). Como tal, la vía B, incluidas las subvías B1 y B2, parece ser completamente viable como la vía metabólica primaria involucrada en la degradación del estireno en S. indicatrix DAI2m / c, capaz de transformar el monómero de estireno en subproductos que posteriormente ingresan a las vías bioquímicas canónicas de producción de energía. Dada la presencia de cinco de los ocho genes, no se puede excluir que la vía A también sea viable en S. indicatrix DAI2m/c, con enzimas alternativas que puedan recuperar la funcionalidad de las tres enzimas no identificadas, pero esta hipótesis necesita una mayor confirmación.
El análisis comparativo del genoma realizado entre S. indicatrix DAI2m/c y S. indicatrix DAIF1 facilitó la identificación de similitudes genómicas. Los genes que codifican enzimas del mapa de estireno presentes en ambas cepas exhiben una pequeña variación de identidad entre las dos cepas (Fig. 3). Además, S. indicatrix DAI2m/c, a diferencia de S. indicatrix DAIF1, alberga un plásmido que transporta muchos elementos similares a fagos (Fig. 1). Los fagos y sus remanentes han sido identificados durante mucho tiempo como contribuyentes significativos para el desarrollo de biopelículas en varios géneros22,23. Significativamente, se ha demostrado que los genes de lisis del profago Lambda defectuoso DLP12 son importantes para la producción de fibra rizada, que, debido a sus propiedades adhesivas y su participación en las interacciones célula-célula y célula-superficie, son fundamentales para la formación de biopelículas en Escherichia coli K-1223. Los genes de lisis DLP12 muestran una alta homología con sus homólogos que están presentes en el casete de genes de lisis SRRz del bacteriófago Lambda24. La presencia de secuencias de lisis viral similares en varias localizaciones del genoma de S. indicatrix DAI2m/c podría contribuir a la liberación del ADN necesario para un desarrollo adecuado de la biopelícula en una superficie de poliestireno. De hecho, se ha demostrado que el ADN extracelular es una característica común de las biopelículas formadas por muchas especies bacterianas; se informó que la actividad de una endolisina profagoica críptica era esencial para la biogénesis de vesículas de membrana bacteriana y biopelículas en Pseudomonas aeruginosa25, y en la última década, se han sucedido artículos que informan sobre profagos que mejoran la formación de biopelículas al facilitar la liberación de ADN26.
El principal resultado de este estudio es la identificación de la cepa DAI2m/c de S. indicatrix como potencial candidata para la degradación del estireno. Los análisis genómicos y bioinformáticos no solo describieron su genoma, sino que también revelaron vías intracelulares no reportadas previamente relacionadas con la degradación del estireno en esta bacteria. Los hallazgos de este estudio establecen una base sólida para futuras investigaciones destinadas a generar datos cuantitativos sobre la degradación del estireno y realizar experimentos genéticos para ampliar nuestra comprensión sobre los roles funcionales de estos genes de degradación de estireno identificados. Las investigaciones futuras también podrían explorar enzimas extracelulares que puedan dirigirse a toda la cadena de poliestireno y realizar más análisis de metabarcoding de la microbiota intestinal en insectos que se alimentan de poliestireno para estudiar su composición en diversas condiciones experimentales. Estos experimentos podrían proporcionar una visión más profunda del potencial de biodegradación total de la cepa DAI2m/c de S. indicatrix, mejorar la comprensión de los procesos de degradación microbiana y ayudar a identificar otros candidatos potenciales para la biorremediación de poliestireno.
Información tomada de la Revista Nature.